新的可编程DNA纳米系统设计用于低成本分子检测
By LabMedica International staff writers
Posted on 06 Sep 2016
基于DNA互补链间自组装力的一种新方式,研究人员开发了一种可编程纳米系统,现已用于一项针对于埃博拉病毒诊断潜力的原理循证研究。Posted on 06 Sep 2016
纳米机械基于“DNA工作的魔力”,Iowa State University(Ames,IO,USA)的教授,Erik R. Henderson博士说明。Henderson教授和校友Divita Mathur博士开发了一种系统,并确定其首项应用:在埃博拉病毒基因检测中的应用。此设备将为稀缺医疗诊断设备的发展中国家提供有价值的服务。此纳米技术设备制造成本低,易于配置和安装。与智能手机应用程序联用,可不依赖传统的医疗设备检测埃博拉病毒或其他病原体和疾病。
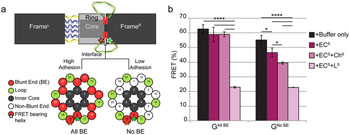
图片:碱基堆集粘附力与OPTIMuS传动器(a)环和骨架间的界面显示为OPTIMuS的横截面。可以通过共轴平端(BE)创建高粘附性或非平端令粘附性最小化进行改良。(b)FRET输出所有平端(所有BE)与非平端(非BE)OPTIMuS,增加额外的不同力量域(****显示P ≤ 0.0001;*显示P ≤ 0.05)(照片由Scientific Reports提供)。
从技术角度来看,他们利用单链和双链DNA的持久长度(“刚度”)差异引出一个自组装DNA纳米系统的一种定义的物理状态变化,这个平台被称为OPTIMuS(询问分子系统的寡推进技术)。这种可诱导的状态变化可以用来在OPTIMuS内询问用户编程的分子相互作用。在这项研究中,他们显示了OPTIMuS如何用于检测可溶的靶分子和评估非共价(碱基堆集)分子相互作用的相对强度。他们应用一种嵌入光子系统检测是否存在靶分子,依据检测情况光子系统进行闪光,可在荧光计上读取闪光情况。
这种技术能改良以检测其他病原体和其他种类的分子。Henderson教授还设想开发相似的纳米机器,能封装药物,向靶点传递。
本研究已由Mathur D & Henderson ER发表于2016年6月7日网络版的Scientific Reports(科学报告)杂志。
Related Links:
Iowa State University




.jpg)






